Zellen in extrem hoher Auflösung
Schnelle Mikroskopiemethode erreicht sehr hohe Ortsauflösungen von besser als zehn Nanometern.
Fortschritte in der Fluoreszenzmikroskopie ermöglichen es, biologische Prozesse unterhalb der klassischen Beugungsgrenze des Lichtes sichtbar zu machen. Eine Variante dieser Superauflösungstechniken ist DNA-PAINT, die von Ralf Jungmann, Forschungsgruppenleiter für Molekulare Bildgebung und Bionanotechnologie am Max-Planck-Institut für Biochemie und Kollegen entwickelt wurde. „DNA-PAINT ermöglicht es, superaufgelöste Bilder mit technisch vergleichsweise einfachen Mikroskopen zu erhalten“, sagt Jungmann. Um das zur Rekonstruktion superaufgelöster Bilder notwendige Blinken von Zielmolekülen zu erreichen, werden diese bei DNA-PAINT mit kurzen DNA-Strängen markiert. In Lösung befindet sich ein komplementärer, farbstoffmakrierter DNA-Strang, der wiederholt an den Zielstrang an- und abbindet und das Ziel zum Blinken bringt. So erreicht DNA-PAINT sehr hohe Ortsauflösungen von besser als zehn Nanometern und kann durch die Nutzung verschiedener DNA-Sequenzen, quasi Barcodes, viele Zielmoleküle gleichzeitig abbilden.
„In den letzten Jahren haben wir die Technik in vielen Bereichen verbessert. Eine große Einschränkung hat uns jedoch immer daran gehindert DNA-PAINT für biologisch relevante Hochdurchsatzstudien einzusetzen: Die vergleichsweise langsame Bildaufnahme“, sagt Jungmann. Klassische DNA-PAINT-Experimente nehmen üblicherweise mehrere zehn Minuten bis hin zu Stunden in Anspruch. „Wir haben uns genau angeschaut, warum das so lange dauert“, so Florian Schüder, Mitarbeiter im Labor von Jungmann. „Durch optimiertes DNA-Sequenzdesign und verbesserte Pufferbedingungen konnten wir die Geschwindigkeit um einen Faktor Zehn erhöhen“, so Schüder weiter.
Hierzu haben die Forscher in Kollaboration mit der Abteilung von Petra Schwille den Einfluss der DNA-Sequenz und der Basenabfolge auf die Geschwindigkeit der Hybridisierung, also das Ausbilden der Doppelhelix, untersucht. Der farbstoffmarkierte Einzelstrang, bei DNA-PAINT auch Imager genannt, besteht generell aus den Grundbausteinen der DNA, den vier Basen: Adenin (A), Thymin (T), Guanin (G) und Cytosin (C). Der Einfluss der Basenkomposition und Länge der Einzelstränge auf die Bindezeit ist recht gut verstanden: Je länger der Doppelstrang und je mehr GC-Basenpaare in der Sequenz vorhanden sind, desto stabiler ist der DNA-Duplex und desto länger die Bindezeit. Der Einfluss auf die Geschwindigkeit der Duplexbildung, und damit die Blinkgeschwindikgeit in DNA-PAINT, ist jedoch deutlich schlechter untersucht. Hier konnten die Forscher nun zeigen, dass die Ausbildung intramolekularer Haarnadelkonformationen, also das Falten mit sich selbst, in kurzen Strängen durch die Reduktion auf zwei Basen vollständig unterbunden werden kann. „Wir haben jetzt die Stränge so entworfen, dass wir nur ein sogenanntes Zweibuchstabenalphabet, etwa nur T und C oder nur A und G, benutzen. So konnten wir die Bindefrequenz bereits um einen Faktor Fünf steigern“, erklärt Schüder. „Durch weitere Optimierungen am verwendeten Puffersystem konnten wir zusätzlich einen Faktor Zwei rausholen, so dass wir jetzt zehnmal schneller Bilder aufnehmen können“.
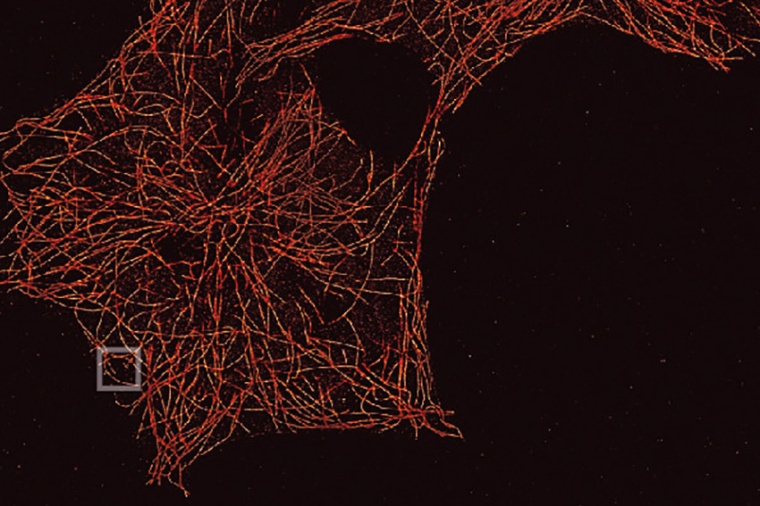
Um die Verbesserungen der DNA-PAINT-Technik zu testen, kombinierten die Forscher diese mit DNA-Origami-Strukturen. Hierbei handelt es sich um selbstassemblierende DNA-Objekte in Nanometergröße, die sich autonom zu einer Art Steckplatte falten. Auf dieser befinden sich die Gegenstränge, die als definierte Punkte im Abstand von ungefähr fünf Nanometern aufgetragen sind. Unter dem Mikroskop untersuchten die Forscher so die verbesserte Messgeschwindigkeit unter definierten Bedingungen. Im nächsten Schritt konnte die verbesserte Aufnahmegeschwindigkeit auch in zellulärer Umgebung gezeigt werden. Hierzu wurden in einer Zellprobe die Mikrotubli, ein Teil des Zytoskelettes, mit zehnfach höherer Geschwindigkeit sichtbar gemacht. „Wir konnten so ein quadratmillimetergroßes Areal in acht& Stunden bei einer Auflösung von zwanzig Nanometern aufnehmen. Das hätte vorher fast vier Tage gedauert“, sagt Florian Schüder. Laut Ralf Jungmann eröffnet sich mit der gezeigten zehnfach höheren Abbildungsgeschwindigkeit ein neues Kapitel superaufgelöster DNA-basierter Mikroskopie. Dies sollte es erlauben, DNA-PAINT für Hochdurchsatzstudien mit biologischer und biomedizinischer Relevanz etwa in der Diagnostik einzusetzen.
MPI Biochemie / JOL